Gene tinkering
„Gene tinkering“ bedeutet „Flickschusterei mit Genen“. Einbau von Genen in andere, bereits bestehende genetische Zusammenhänge soll eine mögliche (Teil-)Erklärung für makroevolutive Veränderungen liefern. Auf diese Weise könnten genetische Netzwerke entstanden sein. Solche Vorgänge sind bislang jedoch weitgehend hypothetisch und sie erklären nicht die Herkunft der Gene an sich. Interessant ist in diesem Zusammenhang der Befund, dass biologische Netzwerke solchen Netzwerken gleichen, die durch Ingenieure erdacht wurden – ein Befund, der ein undurchdachtes gene tinkering in Frage stellt.
1.0 Inhalt
In diesem Artikel wird erklärt, was „gene tinkering“ ist und weshalb dieser weitgehend hypothetische Prozess als mögliche Erklärung für makroevolutive Prozesse angesehen wird. Weiter wird erläutert, weshalb gene tinkering nach derzeitigem Kenntnisstand nichts Wesentliches zum Verständnis von Makroevolution beitragen kann.
1.1 Einleitung
Die Proteine [= Eiweiße] der Lebewesen bestehen häufig aus denselben Abfolgen von Aminosäuren. Man nennt solche Abschnitte Motive oder Domänen. Erstaunlicherweise kommen Proteindomänen (und die zugrundeliegenden Genabschnitte) im ganzen Organismenreich immer wieder in ähnlicher oder sogar gleicher Form vor, jedoch oft in ganz unterschiedlichen Funktionszusammenhängen.
Ein Beispiel: Die CSP-Proteindomäne aus ca. 70 Aminosäuren wurde zuerst in Bakterien entdeckt und wirkt dort als Kälteschutzprotein („cold shock protein“), indem es an Nukleinsäuren bindet. Erstaunlicherweise findet sich das CSP-Motiv auch in (fast) allen anderen Lebewesen. Auch dort bindet die CSP-Domäne an Nukleinsäuren (DNS oder RNS). Doch sie schützt dort nicht gegen Kälte, sondern reguliert durch ihre Anlagerung andere Gene. Außerhalb von Bakterien tritt die CSP-Domäne nur mit anderen Motiven „zusammengeflickt“ auf (Abb. 193). Dasselbe Motiv kommt also in sehr verschiedenen Funktionszusammenhängen in den unterschiedlichsten Organismen vor.

Abb. 193: Beispiele von Proteinen, die die CSP-Domäne (grün) enthalten. Die alleinige CSP-Domäne kommt in Bakterien als Kälteschutzprotein vor, die CSP-Domäne zusammen mit anderen Domänen dagegen in Mehrzellern. Die Y-box, Lin28 und Glycin-reichen Proteine sind zum großen Teil Regulatoren für andere Gene. Die Funktion des UNR-Proteins ist noch nicht genau bekannt, vermutlich ebenfalls ein Regulator. (Nach Graumann & Marahiel 1998)
Es gibt zahlreiche Beispiele dieser Art. Gleiche oder ähnliche Gene können in verschiedenen Organismen im selben oder völlig unterschiedlichen Funktionszusammenhängen zu finden sein, dabei können die Organismen relativ nah oder auch sehr entfernt verwandt sein. In anderen Fällen sind zwar die Funktionszusammenhänge prinzipiell gleich, jedoch die dabei beteiligten Proteine sind völlig verschieden (vgl. dazu auch die häufige Nicht-Entsprechung von Genen, Abläufen in der individuellen Entwicklung (Ontogenese) und Adultorganen [= ausgewachsene Organe], s. den Artikel „Ähnlichkeiten in der Morphologie und Anatomie“ (https://genesis-net.de/e/1-3-e/5-1/)).
Insgesamt hat sich herausgestellt, dass der Unterschied zwischen zwei Organismen folglich nicht so sehr in der Anzahl verschiedener Gene, sondern im unterschiedlichen Zusammenbau gleicher oder ähnlicher Gene oder Genabschnitte besteht. „Die gesamte lebende Welt lässt sich also mit einer Art riesigem Baukasten vergleichen“ (Jacob 2000).
1.2 Evolution durch „Flickschusterei“?
Wie kam es zu diesen unerwarteten Kombinationen? F. Jacob vermutete als erster unbekannte evolutive Prozesse, die bestehende Domänen aneinander „geflickt“ oder Proteine in neue Funktionszusammenhänge eingeschleust haben. Diese weitgehend hypothetischen Vorgänge werden unter gene tinkering („Flickschusterei“ mit Genen) subsummiert; eine allgemein verwendete Definition für diesen Begriff gibt es allerdings nicht. Im Falle der oben erwähnten CSP-Domäne wird spekuliert, dass das ursprüngliche CSP im Laufe der Evolution immer wieder in neue Funktionszusammenhänge gestellt wurde, wobei ihre Nukleinsäurebindefunktion durch Zusammenstellung mit anderen Domänen in eine Gensteuerungsfunktion abgewandelt wurde.
Bislang gibt es nur wenige direkte Beobachtungen solcher Vorgänge und sie erscheinen vergleichsweise einfach; z. B. ist das Gen jingwei einer Fruchtfliegenart nachweislich aus zwei anderen Genen zusammengefügt. Höherentwicklung durch gene tinkering belegen solche Fälle allerdings nicht. Eine Einschätzung der evolutiven Möglichkeiten durch gene tinkering ist aufgrund von Datenmangel bislang kaum möglich. Die Problematik stellt sich am Beispiel des Auges wie folgt dar: Es wird vermutet, dass in der Evolution des Auges, von einem einfachen Ausgangsstadium ausgehend, immer wieder neue Gene in die Kaskade der ontogenetischen Augenentwicklung eingefügt wurden, bis schließlich (wie heute bekannt) ca. 2.000 bis 2.500 Gene bei Embryonalentwicklung heutiger Augen mitwirken (vgl. Abb. 194). Wie dieses gene tinkering – durch Mutation und Selektion angetrieben – erreicht worden sein könnte, ist derzeit unbeantwortbar, da viel zu wenig über mögliche Mechanismen und über die Funktion und Interaktion der beteiligten Gene bekannt ist.
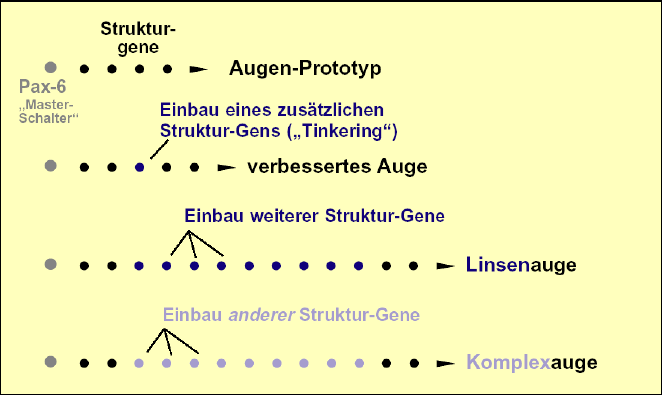
Abb. 194: Stark schematisierte Darstellung des hypothetischen „Gen-Tinkerings“ am Beispiel des Auges. Ein Augen-Prototyp wird zunächst als gegeben vorausgesetzt. Die weitere hypothetische evolutive Entwicklung erfolgt durch sukzessive Einfügung weiterer Gene, die unter der Kontrolle des Master-Gens (Hox-Gen, hier Pax-6) stehen. Die verschiedenen Augentypen sollen demnach durch unterschiedlichen Einbau untergeordneter Gene entstanden sein. Das Hox-Gen bleibt dasselbe und kann daher die Entwicklung verschiedener Augentypen induzieren.
Zudem bleibt die Frage, woher Domänen und funktionelle minimale Anfangszustände kommen, weiterhin offen. Jeder Baustein, der bei einem evolutiven tinkering verwendet wird, muss ja irgendwann einmal entstanden sein. Die Annahme, dass die benötigten Domänen in einem anderen Zusammenhang evolviert seien, verschiebt nur das Problem: „Wie ist die entsprechende Domäne in dem anderen Zusammenhang evolviert?“ Beim oben erwähnten Beispiel des Auges ist auch der einfachste anzunehmende (hypothetische!) Startpunkt für ein prototypisches Auge bereits eine komplexe Struktur. Woher diese kommt, kann durch gene tinkering nicht erklärt werden und wird laut Gehring & Ikeo (1999) dagegen auf zufällige(!) Prozesse zurückgeführt.
1.3 Netzwerke
Komplexe biologische Systeme sind gerade wegen ihrer Komplexität nur schwer zu erfassen. Das ist der Grund, warum man bei der vermuteten Evolution von Augen, beginnend bei einer einfachen lichtempfindlichen Zelle bis hin zu den komplizierten Linsenaugen der Wirbeltiere oder den Komplexaugen der Insekten, bislang auf mehr oder weniger gut begründete Vermutungen angewiesen ist. Neben der Entstehung von Organen entziehen sich auch biochemische Abläufe in den Zellen mit ihrer schier unübersehbaren Menge an Reaktionen unserem Vorstellungsvermögen. Es gibt zwar schon seit einigen Jahren großformatige Poster mit den wichtigsten biochemischen Reaktionen in Pflanzen- und Tierzellen, doch bleiben viele Details außen vor. Als neue Darstellungsformen für komplexe biologische Systeme breiten sich Netzwerk-Darstellungen immer mehr aus. Pfeile geben Richtungen von Interaktionen an und diese können verschieden breit gestaltet werden. Computerunterstützte Systeme können diese Netzwerke darstellen und Analysen zulassen.
In der Technik hingegen werden seit längerem komplexe Systeme mit Erfolg in Form von Netzwerken dargestellt. Interessanterweise kommt nun genau von dieser Seite Kritik am Modell der Evolution als „Kesselflicker“ (gene tinkering). Worin unterscheidet sich das Produkt von jemandem, der an einem Netzwerk so lange herumflickt, bis es zufriedenstellend funktioniert, vom Produkt eines Ingenieurs? Ein Ingenieur würde Strukturen im Voraus planen und Konstruktionspläne zeichnen. Ein Bastler (ein blinder Uhrmacher, um mit Dawkins (1990) zu reden) würde nehmen, was gerade zur Hand ist, um irgendwelche Interaktionen zu erstellen und solange herumflicken, bis sie gut genug sind, um zu funktionieren. Alon (2003) schreibt dazu (in Übersetzung): „Es ist deshalb erstaunlich, dass die Lösungen, die durch die [biologische] Evolution gefunden wurden, viele Gemeinsamkeiten mit einem guten technischem Design besitzen.“ Die drei wichtigsten Prinzipien, die für biologische und technische Netzwerke gleichermaßen gelten, sind:
- modularer Aufbau
- Robustheit gegenüber Bauteiltoleranzen, und
- die Verwendung wiederkehrender Elemente.
1.4 Module und Wiederverwendung
Die „Verwendung wiederkehrender Elemente“ beinhaltet genau jenes Phänomen, das Jacob veranlasste, von einem „Baukasten“ zu sprechen. Auch das erste genannte Prinzip biologischer Netzwerke, die Modularität, weist in jene Richtung. Warum ist es daher erstaunlich, dass technische (von einem Ingenieur erstellte) und biologische (angeblich evolutiv entstandene) Netzwerke sich einander ähneln?
Es gibt in den Computerwissenschaften den Versuch, künstliche „neuronale Netzwerke“ durch einen evolutiven Prozess zu optimieren. Diese neuronalen Netzwerke verarbeiten Information (Input) zu einem gewünschten Ergebnis (Output). Ungleich echten biologischen Netzwerken sind diese künstlichen neuronalen Netze aber nicht modular. Jeder Knotenpunkt in diesem Netzwerk nimmt an vielen verschiedenen Aufgaben teil (Abb. 195a), während in modularen Netzwerken sozusagen „Unternetzwerke“ existieren, die nur mit sehr wenigen Verbindungen in das gesamte Netzwerk eingefügt sind (Abb. 195b). Gleichzeitig stellt man fest, dass künstliche neuronale Netze (mit ihrer nicht-modularen Struktur) besser für eine gewünschte Aufgabe geeignet sind als vergleichbare modulare Netzwerke. Ein solches Netzwerk, in der jede Komponente mit jeder anderen optimal verknüpft ist, kann sich jedoch kaum mehr neuen Bedingungen (z. B. veränderte Umwelt) anpassen, das Netzwerk erscheint „eingefroren“ (Alon 2003; Abb. 195a). In modularen Netzwerken hingegen, wie sie in Lebewesen und technischen Systemen vorkommen, können einzelne Komponenten (die Module oder wiederkehrende Einheiten) ausgetauscht oder verändert werden, um sich neuen äußeren Bedingungen anzupassen.

Abb. 195: Nicht-modulare (a) und modulare Netzwerke (b).
Ein Beispiel: Ist im Computer das Modul „Festplatte“ zu klein, so kann eine neue, größere problemlos eingebaut werden. Ein Beispiel aus der Bakterienwelt wäre die Erschließung einer neuen Nahrungsquelle durch Abwandlung vorhandener Stoffwechselwege. In beiden Fällen ermöglicht erst die Modularität den einfachen Wechsel, bzw. kann man deutlicher formulieren: Modulare Netzwerke sind notwendige Voraussetzungen für mikroevolutiven Wandel von Lebewesen. Gleichzeitig stellte man fest, dass Netzwerke, die durch eine Labor-Evolution entwickelt wurden, eben nicht modular aufgebaut sind, so dass Wissenschaftler ernüchtert feststellen: „[…] die Frage, wie Modularität in der Natur entstanden ist, hat sich zu einem kritischen Punkt entwickelt“ (zitiert nach Lipson et al. 2002).
In der Summe lässt sich festhalten, dass bei genauerer Betrachtung eben jenes von Jacob beobachtete Baukastensystem in Lebewesen (entspricht „modularen Netzwerken“) eher für einen Designer sprechen als gegen ihn. Netzwerke, die im Computer evolviert wurden, funktionieren zwar besser (erscheinen daher dem oberflächlichen Betrachter als weniger „hingeschustert“), sie sind aber nicht modular, und damit weder fehlertolerant noch flexibel genug, um Lebewesen die notwendige Anpassung (= Mikroevolution) zu ermöglichen. Die Frage nach der Makroevolution, also der Entstehung neuer Strukturen (oder Modulen), nicht deren bloße Abwandlung, bleibt weiterhin unbeantwortet, und Alon (2003) formuliert – mit eigenen Worten: „Es erhebt sich [daraus] eine fundamentale wissenschaftliche Herausforderung: Diejenigen Naturgesetze zu verstehen, die evolvierte und kreierte Systeme miteinander verbinden.“ Könnte es nicht umgekehrt sein, dass sich natürliche (angeblich evolvierte) und technische (kreierte) Systeme deshalb so verblüffend ähneln, weil beide geschaffen wurden?
Literatur
Alon U (2003) Biological networks: The tinkerer as an engineer. Science 301, 1866-1867.
Dawkin R (1990) Der blinde Uhrmacher. München.
Gehring W & Ikeo K (1999) Pax 6 masterin eye morphogenesis and eye evolution. Trends Genet. 15, 371-377.
Graumann P & Marahiel M (1998) A superfamily of proteins that contain the cold-shock domain. Trends Biochem Sci. 23, 286-290.
Jacob F (2000) Die Maus, die Fliege und der Mensch. München.
Lipson H, Pollack JB, Suh NP (2002) On the origin of modular variation. Evol. 56, 1549-1556.
Neuhaus K (2002) Gene tinkering: Kann in komplexe biologische Systeme neue Information eingeflickt werden? Stud. Int. J. 9, 59-66.
Autor: Niko Winkler, 14.01.2005
Aktualisiert am 07.01.2024 (B. Scholl); © beim Autor; alter Link: 2005, https://www.genesisnet.info/schoepfung_evolution/i41264.php